Para poder hacer una clasificación de los organismos procariotas hay que hacer análisis genéticos, estructurales y de comportamiento. Además, su nomenclatura (su forma de llamarlos) debe cumplir ciertas reglas.
Vamos a ver todo esto, pero antes nos centraremos en las hipótesis sobre la vida de los microorganismos en la tierra primigenia, ya que, a partir de estos microbios primitivos, se forman los árboles filogenéticos a partir de los cuales se generan las clasificaciones actuales de los seres vivos.
Índice de contenidos
La vida microbiana en la tierra en su estado primigenio
La tierra se formó hace 4600 millones de años. Se cree que la vida precelular pudo ser un ‘’mundo de RNA’’, ya que esta molécula tiene, tanto la capacidad de replicarse, como la de catalizar reacciones enzimáticas.
Se puede considerar que la vida surgió hace 3500-3800 millones de años. Esto es debido al hallazgo de unos microfósiles de procariotas hallados en unos estromatolitos del oeste de Australia. Los estromatolitos son un tipo de rocas estratificadas formadas por la incorporación sedimentos minerales sobre poblaciones bacterianas laminadas.
Estos estromatolitos están formados por unas bacterias filamentosas anaerobias y fotótrofas, con fotosíntesis anoxigénica, aparentemente relacionadas con una bacteria fotótrofa anoxigénica actual llamada Chloroflexus. Las cianobacterias y la fotosíntesis anoxigénica se desarrollaron más tarde.
La diversidad microbiana se incrementó a medida que el oxígeno se hizo más abundante (hace 2000 millones de años).
Los eucariotas surgieron a partir de procariotas. La hipótesis más extendida sobre el origen de los eucariotas es la teoría endosimbiótica, que propone que las mitocondrias y cloroplastos surgieron de la incorporación estable dentro de otro tipo de célula. Las mitocondrias provendrían de una bacteria quimioheterótrofa anaerobia facultativa, mientras que los cloroplastos de una bacteria con fotosíntesis oxigénica.
Las mitocondrias surgieron de un grupo de proteobacterias (que es un grupo muy amplio de GRAM negativas), concretamente de la clase alfa (α). Los cloroplastos parece que provienen de un Phylum común con las cianobacterias (tanto cianobacterias como cloroplastos llevan a cabo fotosíntesis oxigénica).
Esta teoría se basa en la fisiología y su metabolismo, además de en la propia secuencia y estructura de mitocondrias y cloroplastos, ya que contienen ribosomas del tipo procariota, y tienen secuencias génicas del RNAr 16S característicos de procariotas. Los ribosomas de mitocondrias y cloroplastos son sensibles a los mismos antibióticos que los de los procariotas. Además, contienen una pequeña molécula de DNA circular, típica de procariotas.
Dentro de esta teoría se han propuesto dos hipótesis:
- El núcleo se originó espontáneamente como respuesta al aumento del tamaño del genoma, antes de adquirir las bacterias que darán lugar a mitocondrias o cloroplastos. Es decir, la endosimbiosis de produciría a partir de una célula nucleada.
- Hipótesis del hidrógeno. Surgió de la asociación intracelular de una α-proteobacteria productora de hidrogeno que actuaria como endosimbionte y formaría una simbiosis con una arquea sin núcleo, que habría actuado como hospedador. La asociación se produce por la necesidad de H2 por parte del hospedador, que lo va a usar como fuente de energía.
Las arqueas no tienen núcleo; entonces esta teoría sostiene que el núcleo se originó después, tras la asociación y transferencia de los genes responsables de síntesis de lípidos desde el simbionte al cromosoma del hospedador. A partir de esa síntesis de lípidos se forma todo el sistema de endomembranas y la membrana nuclear. Esta célula con núcleo y poseedora de mitocondrias habría adquirido después el ancestro de cloroplastos por endosimbiosis.
Lo que está claro es que la célula eucariota es una quimera, ya que tiene características de bacterias y de arqueas. Los eucariotas tienen un tipo de lípidos presentes en bacterias, al igual que su metabolismo energético. Tienen sistemas de transcripción y traducción más parecidos a los de arqueas. Es probable que el proceso evolutivo se prolongara largos periodos de tiempo y que sufriera numerosos arranques en falso y callejones sin salida, además de haber sido un proceso evolutivo no lineal.
El origen de la célula eucariota podemos considerarlo como un punto de partida para la explosión de la diversidad biológica (aparición de los seres pluricelulares, vida animal, fúngica, etc).
Taxonomía
Es la ciencia de la clasificación biológica. Se compone de clasificación, nomenclatura e identificación:
- Clasificación: ubicación de los organismos en grupos, taxones. Se establece en base de semejanza fenotípica y/o parentesco evolutivo común.
- Nomenclatura: se encarga de asignar los nombres a estos taxones, en base a unas normas publicadas. Esto permite disponer de un lenguaje universal entre la comunidad científica.
- Identificación: permite determinar a qué taxón/taxones pertenece un determinado microorganismo.
Sistemática
Es el estudio científico de los microorganismos, cuyo objetivo final es agruparlos taxonómicamente. Abarca disciplina variadas como morfología, biología celular, ecología, etc.
La sistemática es la ciencia que asocia la taxonomía con la filogenia (historia evolutiva de los organismos). El objetivo clave de la taxonomía es la comprensión de la filogenia, ya que la jerarquía taxonómica tiene que reflejar la jerarquía filogenética: agrupar los microorganismos por características comunes implica que ese grupo ha evolucionado a partir de un ancestro común, de tal manera que cada especie retiene características de sus ancestros.
La mayor parte de la información para establecer la filogenia proviene de fósiles, pero los microorganismos no fosilizan con facilidad. A falta de evidencia fósil, en el caso de la filogenia de procariotas; hay que recurrir a otros datos. En el caso de eucariotas, los estudios de secuenciación del DNA concuerdan muy bien con los registros fósiles (que en eucariotas si hay). Esto ha llevado a los científicos a establecer la filogenia de procariotas mediante de estudios de secuenciación y de hibridación.
Para ello eligen determinadas secuencias del genoma: las moléculas elegidas han sido las de RNA, ya que son los mejores cronómetros evolutivos. Más concretamente los RNAr de la subunidad pequeña (SSU rRNA: Small ribosomal Subunit RNA): el 16S en procariotas y el 18S en eucariotas. A partir de ellas se deducen filogenias microbianas.
Están presentes en todos los organismos (tienen distribución universal) y en todos realizan la misma función. Además, como el ribosoma es esencial para la supervivencia, los genes que codifican sus componentes no pueden soportar grandes cambios, ya que resultan letales: los ribosomas tienen una estructura secundaria determinada y muy específica.
Los cambios que se mantienen y que podemos observar han sido cambios muy lentos y muy leves. Esto permite comparar organismos muy separados en la evolución. Además, no están sujetos a transferencia génica horizontal: no se transfieren por plásmidos, debido a que están en el cromosoma.
En base a comparaciones de las secuencias del SSU rRNA se han podido establecer relaciones evolutivas y arboles filogenéticos. Se han creado los tres dominios principales. La longitud de las ramas indica relaciones evolutivas entre organismos, pero no tiempo.
Los árboles filogenéticos se establecen:
- Secuenciando el gen de un organismo concreto que queremos identificar.
- Alineando la secuencia con la de otros organismos para buscar homologías: a mayor homología, mayor parentesco.
- Incluyendo el taxón en un árbol filogenético, que es la representación de líneas de descendencia y la relación entre microorganismos interpretándose en términos de parentesco común. Esta constituido por ramas que conectan nodos.
Un árbol tiene ramas y nodos internos y externos. Pero pueden o no tener raíz, en el sentido de saber cuál es el ancestro común de varias especies, géneros, cepas, etc.
Los nodos donde hay números son especies, cepas, géneros, y etc. Los nodos internos son ancestros, es decir los nodos externos son los actuales. Las ramas determinan el orden de descendencia y los ancestros de los nodos, los que son los ancestros de las cepas actuales. La longitud de esas ramas no indica realmente tiempo sino el número de cambios que se han producido.
Si no hay raíz, el árbol no da una idea evolutiva, solo se establecen relaciones de parentesco. Con raíz se da cierta idea evolutiva.
Construcción de árboles filogenéticos
La distancia evolutiva (relación de organismos) es la forma en la que se indica, cuantitativamente, el número de posiciones que difieren dos secuencias nucleotídicas alineadas. Es decir, indica la relación entre los organismos. La relación se mide en distancia evolutiva. Los organismos se agrupan en función de las semejanzas de sus secuencias.
Hay un método muy empleado para establecer las relaciones filogenéticas: el análisis de parsimonia. Las relaciones se determinan calculando el número mínimo de cambios necesarios para llegar a las secuencias finales que se están comparando, suponiendo que el cambio evolutivo se produce por la vía más corta (menor número de cambios desde el antecesor hasta el organismos en cuestión).
Con el análisis informático del alineamiento de secuencias del SSU rRNA se ha confirmado la presencia de unas secuencias firma: secuencias cortas y conservadas, específicas para un grupo filogenéticamente definido de organismos. Se pueden definir secuencias firma características de dominio, género o especie particular. Ayudan a clasificar organismos aislados recientemente o previamente mal clasificados en su grupo filogenético correspondiente.
Gracias al análisis filogenético se han podido establecer los 3 dominios fundamentales: Bacteria, Archaea y Eukarya.

Los diferentes análisis en la sistemática microbiana
La taxonomía en procariotas se puede considerar taxonomía polifásica: engloba varios métodos con diferentes análisis.
Análisis fenotípico (fenético)
En el análisis fenotípico se tiene en cuenta:
- Propiedades morfológicas
- Características metabólicas, bioquímicas y fisiológicas
- Características serológicas
- Sensibilidad a fagos
Este tipo de análisis tiene en cuenta diferencias metabólicas, estructurales, etc. En estudios clínicos donde es necesario la identificación existen toda una serie de rasgos fenotípicos que permiten, clara y rápidamente, discriminar entre la identificación más probable.
Las características morfológicas establecen morfotipos dentro de una especie. Pero en sí mismas no dan mucha información. Al microscopio óptico dos especies pueden ser muy parecidas morfológicamente; por ejemplo, dos cocos. Por eso puede servir de ayuda el que presente ciertas estructuras como endosporas, flagelos, etc. Las tinciones diferenciales permiten diferenciar algunos grupos de organismos pero no siempre se pueden aplicar ni dan demasiada información; tienen utilidad limitada (por ejemplo, no tiene sentido hacer tinción de GRAM a micoplasmas o arqueas).
Las características metabólicas, bioquímicas y fisiológicas permiten establecer biotipos. Se realiza mediante pruebas bioquímicas o técnicas de quimio taxonomía.
- Pruebas bioquímicas: resultan útiles porque sirven para poder separar géneros o especies a veces estrechamente relacionadas entre sí, para diferenciar dentro de un bloque de organismos, especies o géneros. También suelen emplear sistemas de detección rápida, sobre todo en clínica. En el caso de enterobacterias, tiene carácter taxonómico el uso de un determinado azúcar. Hay unas que fermentan lactosa y otras no.
- Técnicas de quimiotaxonomía: permiten determinar perfiles (de poliaminas, quinonas respiratorias, sideróforos, ácidos grasos,…). Hay una técnica llamada FAME (Fatty Acid Methyl Ester) para identificación rutinaria de patógenos: se basa en el estudio de perfiles de ácidos grasos. La cantidad y el tipo de lípidos son característicos de un determinado género o especie. La técnica FAME se emplea en identificación o en clasificación de microorganismos. Con esta técnica, se extraen ácidos grasos de la bacteria en estudio, se modifican, se forman los esteres metílicos derivados de esos ácidos grasos y se tratan de identificar con cromatografía de gases. Ese perfil se compara con los perfiles de la base de datos.
- También hay técnicas de espectrometría que comparan metabolitos de bajo peso molecular (espectrofotometría de alta resolución: ICR-FT/MS) o de alto peso molecular (espetrofotometría de Maldi-Tof: identificación de aislados clínicos).
Las características serológicas permiten establecer serotipos, como el sistema de Lancefield. Si disponemos del antisuero adecuado con anticuerpos específicos, como la unión antígeno anticuerpo es específica, con esos anticuerpos podremos clasificarlo si se unen al microorganismo.
La sensibilidad a fagos permite establecer fagotipos. Se realiza mediante pruebas de fagotipia: consisten en ensayos en los que se trata de determinar a qué fagos es sensible una determinada bacteria. Los fagos son específicos y suelen infectar a una especie concreta o una variante concreta. Se siembra cada cepa en una placa diferente y se siembra uniformemente la cepa en cuestión. Después, se inoculan los distintos fagos en cada una de las cuadriculas, se incuban las placas y se observa si hay o no lisis. Si el fago ha lisado la bacteria, aparece halo de lisis y quiere decir que la bacteria es sensible a ese fago. Esto permite comparar diferentes cepas por su sensibilidad a fagos.
Análisis genotípico
En el análisis genotípico se estudia:
- Contenido G +C
- Hibridación DNA-DNA (DDH) o DNA-RNA (DRH)
- Huella genómica (perfil de DNA, DNA fingerprinting)
- Ribotipado
- Análisis de secuencias repetitivas de DNA
- AFLP
- MLST (análisis de secuencias multilocus)
Contenido en G+C
El contenido en G+C. Puede fluctuar del 20-80%. Fluctúa más en procariotas que en eucariotas. Es posible que dos organismos puedan tener el mismo contenido de G+C pero ser organismos muy distintos: a partir de una composición de bases muy parecida se pueden obtener secuencias muy diferentes y dar lugar a numerosos organismos.
Realmente el análisis químico del porcentaje G+C no es fiable taxonómicamente, y se está quedando obsoleto: va siendo sustituido por el análisis in silico. Con el tiempo quedará para confirmar la asignación de un organismo a un taxón superior.
Hibridación DDH o DRH
La hibridación DNA-DNA (DDH) se basa en el hecho de que, al calentar el DNA de dos organismos, las dos cadenas se van a desnaturalizar, y el enfriamiento lento permite la renaturalización. Al estar mezclados los DNA de ambos organismos, pueden hibridar siempre y cuando las secuencias sean iguales o similares. El grado de hibridación nos indica el grado de parentesco. Cuanto mayor sea el grado de hibridación mayor es el parentesco.
Se prepara el DNA de ambos organismos. Uno se fragmenta y se marca con fosfato radiactivo. Se desnaturalizan ambos DNA y se mezclan. Siempre hay que añadir una cantidad saturante del DNA sin marcar para evitar que el marcado hibride consigo mismo. A continuación, se separa el DNA hibridado del no hibridado y se mide la cantidad de radiación.
Se interpretan los resultados observando la radiactividad, viendo que el 100% va a ser el DNA que ha hibridado consigo mismo. Dos cepas son de la misma especie si los valores DDH ≥ 70%. Dos cepas son del mismo género si los valores DDH ≥ 25%. Si es menor no pertenecen al mismo género.
Hibridación DNA-RNA (DRH). Estos experimentos también se pueden hacer con DNA de uno y RNA de otro. Estas pruebas permiten la clasificación y también la identificación rápida de algunas bacterias mediante "sondas" adecuadas. Una sonda es una cadena específica de ácido nucléico que, una vez marcada, se puede utilizar para que hibride con su complementaria en una mezcla con ácidos nucléicos.
Por ejemplo, si estamos analizando un alimento para ver si se ha contaminado con Salmonella, lo que se hace es obtener la sonda. El DNA de esta batería se fragmenta con enzimas de restricción y se selecciona un fragmento adecuado, es decir, un fragmento que solo este en Salmonella y no en otras bacterias. Se marca radiactivamente o con fluorescencia. Por otro lado, la muestra de alimento se filtra y las bacterias presentes en el alimento crecen porque se hacen crecer en medio adecuado. Obtenemos cadenas sencillas y si hay DNA de Salmonella la radiactividad o la fluorescencia permite identificar la bacteria.
Huella genómica
Por otro lado, la prueba de la huella genómica no requiere secuenciación de nucleótidos. Se trata de generar patrones de fragmentos de restricción (que son fragmentos de DNA obtenidos con enzimas de restricción) para analizar la semejanza genotípica entre las cepas. Permite discriminar a nivel de especie, subespecie, y a menudo cepa, por lo que es válido en clasificación. Hay distintos métodos:
Ribotipado. Es un método especifico y rápido y se centra en un solo gen, en concreto en el gen que codifica el RNAr de la subunidad pequeña (SSU rRNA). Pasos para el ribotipado:
- Amplificación (PCR) del DNA que codifica SSU rRNA.
- Tratamiento con enzimas de restricción.
- Separación por electroforesis
- Rastreo con sonda marcada de SSU rRNA.
- Digitalización del perfil generado.
- Comparación con perfiles de organismos relacionados (base de datos).
Se trata de amplificar por PCR el DNA que codifica el RNA ribosómico de la unidad pequeña. Se marcan y ya tenemos la sonda marcada. Después, se tratará con enzimas de restricción el genoma del organismo y esos fragmentos se separan por electroforesis. Solamente hibridará donde aparezca su cadena complementaria. Ese perfil va a ser único para una determinada especie bacteriana. Este perfil generado se digitaliza y se compara con otros de otros microorganismos. Hay otros que analizan la variación en la secuencia del DNA en el genoma completo; no se centran en un gen sino en el genoma completo.
Análisis de secuencias repetitivas de DNA. Hay una serie de secuencias en los genomas que están altamente conservadas y de las cuales hay un gran número de copias. Hay 3 grandes familias de secuencias repetitivas: REP-PCR (repetitive extragenic palindromic PCR), ERIC-PCR (enterobacterial repetitive intergenic consensus) , BOX-PCR. Su número y posición difiere entre cepas cuyas secuencias han divergido.
Es una técnica válida en el estudio de la diversidad microbiana e identificación de patógenos. La muestra puede proceder de un individuo que se sospeche que tiene el microorganismo o que lo tengamos aislado en el laboratorio. El proceso comprende 3 partes:
- Amplificación por PCR de las secuencias repetitivas
- Separación y visualización en gel de agarosa. Cada carril corresponde a un aislamiento bacteriano, y se forman patrones similares a códigos de barras.
- Análisis de los patrones en el ordenador, donde hay reconocimiento de patrones y cálculo de las relaciones filogenéticas.
AFLP (Amplified fragment lenght polymorphism). Polimorfismo en la longitud de los fragmentos de restricción amplificados.
El MLST (Multilocus sequence typing; análisis de secuencias multilocus). Permite caracterizar cepas dentro de una misma especie. Tiene un nivel de restricción demasiado elevado, por lo que se usan para proporcionar información a nivel de género y familia: da una excesiva resolución para niveles superiores. Se desarrolló para rastrear cepas patógenas, pero su aplicación se ha extendido a la taxonomía microbiana.
Implica la secuenciación de fragmentos de varios genes esenciales, de mantenimiento básico celular. Son unos 5-10 genes, que van a estar en el cromosoma y no van a estar sujetos a transferencia horizontal. Se comparan con las de genes equivalentes de otras cepas del mismo organismo.
Un alelo del gen se representa con un número. A cada cepa se le asigna un perfil alélico, que es una serie de números (tipificación de secuencia multilocus). Cada perfil alélico define el ‘’tipo de secuencia’’ (ST). Esto establece si entre dos cepas existe algún tipo de relación.
El grado de relación entre los distintos perfiles alélicos se representa en forma de diagramas con forma de árbol (dendrograma).
Distancia 0 = cepas idénticas
Distancia 1 = poco relacionadas.
El problema es la selección de los genes que van a ser comparados. Si no se seleccionan bien los genes puede que no se refleje la auténtica filogenia de ese microorganismo.
Análisis filogenético
En el análisis filogenético se tienen en cuenta los análisis:
- De genes individuales
- De secuencias multigénicas
- Basados en secuencias genómicas completas
Los datos filogenéticos son un componente clave de la taxonomía polifásica. Utiliza las secuencias de múltiples genes a la vez para describir e identificar organismos.
Si realizamos el análisis de genes individuales, vemos que el análisis de SSU rRNA ha permitido establecer relación entre especies. Si dos especies difieren en más de un 3%, no son de la misma especie, ya que su grado de hibridación es menor del 70%. Su poca divergencia limita su eficiencia en la discriminación a nivel de especie. El problema puede evitarse analizando genes con mayor grado de divergencia.
Muchos genes tienen el inconveniente de que se transfieren horizontalmente. Para evitar eso, en filogenia son más frecuentes las estrategias basadas en análisis de secuencias multigénicas. Es similar a la técnica MLST pero con secuencias completas de genes. La secuenciación de genes no relacionados funcionalmente va a permitir:
- Muestrear el genoma de modo más representativo que el comparar un solo gen
- Detectar casos de transferencia horizontal, es decir, si están o no localizados en el cromosoma, y en el caso de que no, se excluye el análisis de la secuencia de eso genes.
El análisis en secuencias genómicas completas es el análisis comparativo de genoma; se compara todo con todo. Proporciona numerosos rasgos para el análisis genotípico comparativo. No está sometido a sesgo en la selección de secuencias ya que se analiza todo contra todo.
Detección de microorganismos no cultivados
Se hace mediante la técnica FISH: hibridación fluorescente in situ. Hace falta disponer de una sonda. El procedimiento lleva 4 pasos:
- Marcaje fluorescente de sonda "filogenética"
- Permeabilización de células (entrada de la sonda)
- Hibridación sonda-rRNA, formando células fluorescentes
- Observación al microscopio de fluorescencia.
El uso de ciertas sondas puede detectar microorganismos no cultivados. Pueden aplicarse directamente:
- A células en cultivo.
- A células en su ambiente natural. Se usa como una tinción filogenética. Evita la necesidad de microorganismos, ya que hay muchos que no pueden ser cultivados en medios sintéticos. Los genes de SSU rRNA amplificados por PCR no necesitan proceder de cultivos puros.
Se emplea habitualmente en:
- Ecología microbiana. Análisis de comunidades microbianas (Seguimiento microscópico directo; composición e interacciones).
- Diagnóstico clínico. Identificación rápida de patógenos en muestras clínicas sin necesidad de cultivos puros.
Nomenclatura científica y clasificación de procariotas
Se basa en el sistema binomial de Linneo. Esta nomenclatura, usada también para describir al resto de seres vivos (aunque con algunas modificaciones), tiene varias reglas:
- Consta de dos nombres: nombre genérico (género) cuya letra inicial se escribe en mayúscula + epíteto especifico (especie) que se escribe en minúscula.
- Ambos nombres deben de escribirse subrayados o en cursiva.
- Normalmente son nombres en latín o griego, o se latinizan añadiendo el sufijo adecuado.
- El nombre genérico sólo se puede abreviar cuando ha sido nombrado antes.
- Las cepas se identifican con letras, número, epítetos que siguen al nombre de especie.
- La nomenclatura está sujeta a reglas estrictas, comprendidas en el Código Bacteriológico.
- Cada especie (taxón básico) se asigna a un género.
- La familia es el taxón superior empleado de modo rutinario.
- Los microbiólogos, con frecuencia, emplean nombres informales; por ejemplo: bacterias rojas, espiroquetas, etc.
Concepto de especie procariota
La especie procariota es un concepto distinto al de especie de organismos superiores. Pero la definición de especie que se da para organismos no es válida en microbiología, ya que en el caso de los procariotas son organismos haploides sin reproducción sexual.
Especie procariota: grupo monofilético de organismos (grupo de cepas) con el suficiente grado de coherencia o semejanza genotípica y fenotípica como para diferenciarse de sus semejantes. Los individuos tienen un cierto grado de diversidad fenotípica interna (variación genética).
Hay dos rasgos genotípicos esenciales para agrupar cepas dentro de una misma especie: semejanza de frecuencia en SSU rRNA y la hibridación de DNA. Si los genes de sus SSU rRNA tienen ≥ 97% de secuencias idénticas (lo que implica un % de G+C similar) y un grado de hibridación del DNA > 70%. dos procariotas pertenecen a la misma especie.
Idealmente una especie también se debería distinguir fenotípicamente de otras especies similares.
Una cepa (estirpe) es una población clonal formada por descendientes de una sola célula, pero sin descartar una divergencia a partir de la parental, originando células distintas. Dentro de una especie se pueden diferenciar morfotipos, biotipos, serotipos y fagotipos.
Un clon es una población de células genéticamente idénticas (iguales y descendientes de una sola célula).
El Manual Bergey y los procariotas
En la sección de bacterias se seguirá una clasificación de acuerdo con la descrita en la segunda edición del Manual de Bergey de Bacteriología Sistemática. Es un tratado esencial sobre la taxonomía de procariotas (bacterias y arqueas). La clasificación se basa en las comparaciones de las secuencias de ácidos nucleicos, en especial las secuencias del SSU rRNA. Consta de 5 volúmenes y engloba 25 filos:
- Volumen I. Arqueas, bacterias fotótrofas y bacterias evolutivamente más antiguas.
- Volumen II. Proteobacterias: alfa (α), beta (β), gamma (γ), delta (δ) y épsilon (ε).
- Volumen III. Bacterias Gram positivas con bajo contenido de G+C. Incluye micoplasmas.
- Volumen IV. Bacterias Gram positivas con alto contenido de G+C.
- Volumen V. 10 filos de bacterias gram negativas no relacionadas entre sí.
La taxonomía es la ciencia (dentro de la biología) que se encarga de ordenar a los seres vivos usando elementos clasificatorios llamados taxones. Vamos a ver como están organizados, además de la forma científica de nombrar a las especies (hay diferencias en función de si es animal, vegetal, bacteria, etc).
Índice de contenidos
Categorías taxonómicas
El orden taxonómico actual, de mayor a menor, es el que aparece en la siguiente imagen.
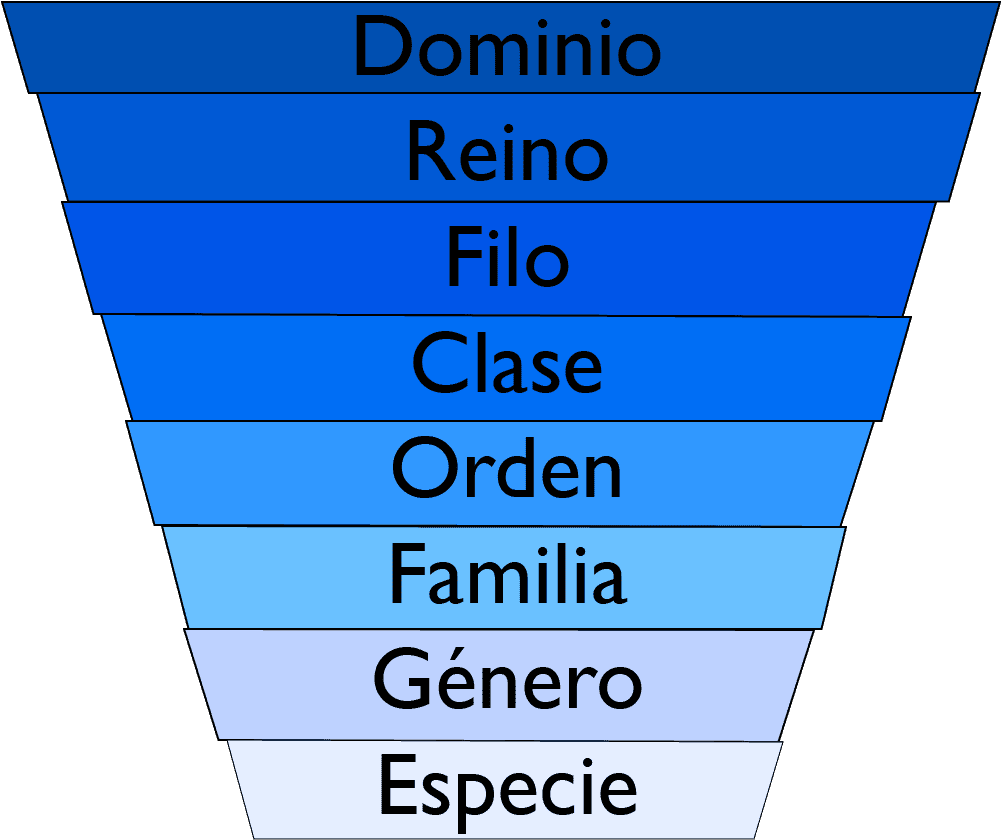
Cada grupo que aparece aquí (dominio, reino, etc) es un taxón. Son grupos de clasificación para los seres vivos que se organizan en función de sus semejanzas físicas y genéticas. Vamos a hablar de las categorías actuales. Y sí, la taxonomía es una ciencia en constante cambio. Sin ir más lejos, hasta hace unos años, tanto Bacteria como Archaea estaban dentro del antiguo reino Monera. No obstante, ahora mismo la organización taxonómica es la siguiente:
- Dominio. Es la categoría que agrupa más seres vivos; los divide por sus características celulares. Así, actualmente hay 3 dominios: Archaea, Bacteria y Eukarya.
- Reino. Este taxón divide a los seres vivos por su naturaleza en común. Archaea y Bacteria son reinos (además de dominios), ya que son unicelulares, procariontes, y tienen otras características bioquímicas y biofísicas que las hacen diferentes. El dominio Eukarya si que se divide en varios reinos, 4 reinos:
- Protista. Organismos unicelulares y pluricelulares que no pueden clasificarse dentro de los otros 3 reinos.
- Fungi. Son los hongos: setas, mohos y levaduras. Organismos heterótrofos con pared celular compuesta de quitina.
- Plantae. Organismos autótrofos, con pared celular compuesta mayoritariamente de celulosa, y sin capacidad de locomoción.
- Animalia. Organismos heterótrofos, sin pared celular, y con capacidad de locomoción.
- Filo (Phylum). Esta unidad divide a los seres vivos por su sistema de organización.
- Clase. Las clases dividen a los seres vivos por las características más comunes que hay entre miembros de un filo.
- Orden. El orden divide a los seres vivos por las características comunes que hay entre miembros de una clase.
- Familia. Las familias dividen a los seres vivos por las características más comunes que hay entre miembros de un orden.
- Género. Este taxón agrupa a especies relacionadas entre sí por medio de la evolución.
- Especie. Es la unidad básica, el grupo de individuos que tiene capacidad de reproducción con descendencia fértil.
Mas adelante veremos varios ejemplos para entender mejor esta clasificación.
Taxones
Dentro de cada taxón pueden haber categorías intermedias (subreinos en un reino, agrupación de familias formando una superfamilia, etc). Estas categorías intermedias son opcionales, y se usan para que la clasificación este mejor organizada y sea más fácil encontrar el taxón de interés en el caso de que haya muchos elementos dentro de un grupo. Esta sería la clasificación taxonómica usando dichas categorias intermedias:
- Dominio
- Subdominio
- Infradominio
- Reino
- Subreino
- Infrarreino
- Superfilo
- Filo
- Subfilo
- Infrafilo
- Superclase
- Clase
- Subclase
- Infraclase
- Magnorden
- Superorden
- Granorden
- Mirorden
- Orden
- Suborden
- Infraorden
- Parvorden
- Superfamilia
- Familia
- Subfamilia
- Tribu
- Subtribu
- Género
- Subgénero
- Especie
- Subespecie
Códigos de nomenclatura
Pueden variar en función de si son animales, plantas o bacterias; de hecho, hay códigos de nomenclatura cada uno de éstos. Actualmente, tenemos estos códigos de nomenclatura:
- Código Internacional de Nomenclatura Zoológica (animales).
- Código Internacional de Nomenclatura Botánica (algas, hongos y plantas).
- Código Internacional de Nomenclatura de Bacterias (bacterias). "The Taxonomic Outline of Bacteria and Archaea" (TOBA). Engloba a los procariotas, tanto arqueas como bacterias. En este artículo puedes ver los análisis filogenéticos que se llevan a cabo para la clasificación de procariotas.
- Código Internacional de Nomenclatura de Virus (virus). Si bien no son considerados seres vivos, cabe recalcar que tienen su código de nomenclatura.
Ahora bien, también hay clasificaciones en función de su forma de vida, de su metabolismo, etc. Por ejemplo, se pueden clasificar a los seres vivos en función de su fuente de energía, poder reductor y carbono.
Código Internacional de Nomenclatura Zoológica
Se encarga de establecer normas para un correcto nombramiento de los animales, dando así una forma común para todos los zoólogos del mundo. Los nombres se dan en latín. Hay terminaciones específicas para el Reino Animalia que afectan a los taxones inferiores a familia (incluyendo familia).
- Superfamilia (-oidea). Para referirnos a la superfamilia en español podemos usar la terminación -oideos.
- Familia (-idae). Para referirnos a la superfamilia en español podemos usar la terminación -idos.
- Subfamilia (-inae). Para referirnos a la superfamilia en español podemos usar la terminación -inos.
- Tribu (-ini). Para referirnos a la superfamilia en español podemos usar la terminación -inis.
- Subtribu (-ina). Para referirnos a la superfamilia en español podemos usar la terminación -ina.
Los taxones superiores no tienen terminaciones específicas. Así, los filos Porifera o Cnidaria, las clases Calcarea o Hydrozoa, o los órdenes Clathrinida o Lemnomedusae no tienen terminaciones comunes. Pueden aparecer terminaciones comunes dentro de un taxón, pero no todos los filos, clases y órdenes tienen las mismas terminaciones.
Código Internacional de Nomenclatura Botánica
Este código da una forma común de nombrar a los taxones de los reino Plantae, Protista y Fungi. En el siguiente recuadro se pueden ver las terminaciones que aparecen en estos reinos. Como se puede ver, hay terminaciones comunes para determinados taxones.
| Categoría taxonómica | Plantae | Protista | Fungi |
| Filo | -phyta | -mycota | |
| Subfilo | -phytina | -mycotina | |
| Clase | -opsida | -phyceae | -mycetes |
| Subclase | -idae | -phycidae | -mycetidae |
| Superorden | -anae | ||
| Orden | -ales | ||
| Suborden | -ineae | ||
| Infraorden | -aria | ||
| Superfamilia | -acea | ||
| Familia | -aceae | ||
| Subfamilia | -oideae | ||
| Tribu | -eae, -ae | ||
| Subtribu | |||
Código Internacional de Nomenclatura de Bacterias
Las terminaciones del Reino Bacteria son:
- Orden. -ales
- Suborden. -ineae
- Familia. -aceae
- Subfamilia. -oideae
- Tribu. -eae
- Subtribu. -inae
La nomenclatura binaria
Este método de nomenclatura se basa en dos nombres, llevando el primero la letra inicial en mayúscula, mientras que el segundo está en minúsculas (Escherichia coli, Canis lupus). Es el científico sueco Carl von Linneo quien comienza a generalizar el uso de esta forma de nomenclatura.
Cada especie tiene un nombre compuesto por dos partes:
- La primera palabra hace referencia a su género (Escherichia, Canis)
- La segunda palabra hace referencia a su especie (coli, lupus)
También pueden escribirse con 3 palabras; en ese caso estaríamos hablando de nomemclatura trinomial. Se usan para nombrar una subespecie dentro de una especie. Así, por ejemplo, podemos diferenciar al lobo ibérico (Canis lupus signatus) del lobo común (Canis lupus lupus).
Los nombres se escriben en latín y no van acompañados de artículos. Siempre que se escriban deben resaltarse, así que normalmente aparecen en cursiva. Esto es sencillo en documentos web; en caso de escritura a mano se puede subrayar (Canis lupus). Si usamos el nombre común y el científico de una especie a la vez el nombre científico aparece entre paréntesis. Ejemplo: El lince ibérico (Lynx Pardinus) es una especie endémica de la península ibérica.
Además, se debe escribir el nombre completo la primera vez que hablamos de dicha especie; en las siguientes veces siguientes que nos refiramos a dicha especie podemos usar su forma abreviada. Así, ahora sería correcto escribir E. coli o C. lupus, ya que hemos escrito su nombre completo anteriormente.
Ejemplos de clasificación taxónomica
Si estudias biología en la universidad casi que, con total seguridad, vas a tener que aprender usar esta clasificación. Ese examen es conocido como visu (palabra del latín, cuyo significado es "visto directamente"). Este examen suele hacerse en zoología y botánica. En ese examen te pedirán, como máximo, los 8 principales taxones de clasificación, si bien normalmente pedirán los taxones descendentes a partir del filo (6 taxones). No obstante, en alguno de los ejemplos que vamos a ver usaremos también algún taxón intermedio (y así verás que pueden ser bastante útiles). Verás que se suele escribir en forma de lista, y los taxones van en orden descendente. No obstante, el género no se escribe solo; va acompañado del nombre de la especie en cuestión, usando la nomenclatura binaria. Vamos a explicar las características de los taxones que se usen.
Vamos a ver su uso con las siguientes especies: El elefante asiático (Elephas maximus), el búho real (Bubo bubo), el camarón gris (Crangon crangon), el bígaro común (Littorina littorea), La carabela portuguesa (Physalia physalis) y la lavanda común (Lavandula angustifolia).
Las primeras 5 especies entran dentro del reino Animalia, mientras que la lavanda está en el reino Plantae. Ahora viene la lista de dichas especies:
Elephas maximus
- Filo Chordata. Se caracteriza por tener una cuerda dorsal (notocorda), un cordón nervioso en posición dorsal, hendiduras faríngeas y cola. Todos los animales cordados han tenido estos elementos al menos en alguna fase del desarrollo embrionario.
- Subfilo Vertebrata. Se caracteriza por tener espina dorsal o columna vertebral. Son los animales vertebrados.
- Clase Mammalia. Animales de sangre caliente con glándulas mamarias productoras de leche con las que alimentan a sus crías.
- Orden Proboscidea. Animales de gran talla, piel gruesa, escaso pelaje y con probóscide (trompa). Agrupa a los elefantes.
- Familia Elephantidae. La familia de los elefantes.
- Elephas Maximus. El elefante asiático. La principal diferencia de este respecto al elefante africano (Loxodonta africana) son las orejas: el elefante asiático tiene unas orejas muy pequeñas en comparación al africano.
Bubo bubo
- Filo Chordata. Ya explicado
- Subfilo Vertebrata. Ya explicado.
- Clase Aves. Animales de sangre caliente, con plumas recubriendo su cuerpo, con pico, que se mueven en tierra con sus extremidades posteriores, y cuyas extremidades anteriores son alas.
- Orden Strigiformes. Aves rapaces nocturnas en su mayoría.
- Familia Strigidae. Grupo en el que se incluye a búhos, mochuelos, cárabos, etc.
- Bubo bubo. El búho real.
Crangon crangon
- Filo Arthropoda. Animales invertebrados con esqueleto externo y apéndices articulados.
- Subfilo Crustacea. Caracterizados por tener dos pares de antenas y apéndices birrámeos.
- Clase Malacostraca. Formados por 14 segmentos organizados en 3 tagmas (regiones): céfalon (cabeza) con 5 segmentos, tórax con 8 segmentos y pleon (abdomen) con 6 segmentos.
- Orden Decapoda. Crustáceos con 10 patas.
- Familia Crangonidae. Animales de tamaño pequeño, bentónicos y nocturnos.
- Crangon crangon. Camarón gris.
Littorina littorea
- Filo Mollusca. Animales invertebrados de simetría bilateral no segmentados, de cuerpo blando, desnudo o protegido por una concha.
- Clase Gastropoda. Animales con área cefálica (cabeza), concha dorsal y pie musculoso ventral.
- Orden Littorinimorpha. Animales principalmente marinos con branquias y opérculo.
- Familia Littorinidae. Moluscos con concha lisa, pequeña o muy pequeña, con o sin una espira alta, generalmente coloreada. Con ornamentación a base de líneas gruesas, sin costillas espirales, ni ombligo. El opérculo tiene una espiral de 2 o 3 vueltas.
- Littorina littorea. Bígaro común. Concha con altura de entre 2 y 4 cm, de color gris pardusco o gris verdoso, con bandas en espiral de tonalidad más clara.
Physalia phisalis
- Filo Cnidaria. Animales invertebrados con simetría radial, cuerpo en forma de saco y células urticantes llamadas cnidocitos.
- Clase Hydrozoa. Tienen formas pólipo y forma medusa. Las medusas tienen velo, las gónadas son siempre de origen ectodérmico, y la mesoglea de los pólipos está poco desarrollada.
- Orden Siphonophorae. Cnidarios que forman colonias flotantes.
- Familia Physaliidae. Engloba 4 organismos que forman colonias.
- Physalia phisalis. La carabela portuguesa. Tiene una vela en su parte flotante que le permite desplazarse por el mar.
Lavandula angustifolia
- Filo o división Magnoliophyta. Plantas florales.
- Clase Magnoliopsida. Plantas florales dicotiledóneas.
- Orden Lamiales. Plantas con flores de corolas bilabiadas, simétricas y bilaterales. Estas tienen 5 pétalos y un ovario compuesto por 2 carpelos fusionados.
- Familia Lamiaceae. Agrupa 245 géneros y más de 7.000 especies.
- Lavandula angustifolia. Planta con tallos cuadrados, algo pelosos. Las hojas son agudas, enteras y verdes. La inflorescencia es espiciforme y pedunculada. Las flores tien un cáliz peloso. La corola tiene el labio superior bilobulado (2 lóbulos) y el inferior con 3 lóbulos más pequeños que los del labio superior. Dichos lóbulos son de color lila.
La clasificación del Comité Internacional de Taxonomía de Virus (siglas ICTV en inglés) utiliza una forma de clasificar muy parecida a la que se hace con los seres vivos. Así, los virus se clasifican por orden, familia, subfamilia, género y especie.
Los virus se clasifican en 4 dominios, 9 reinos y 16 filos, además de 1 orden, y diversas familias y géneros que no están englobados en ningún dominio.
El dominio Duplodnaviria engloba virus ADN de doble cadena que codifican la cápside proteica HK97.
El dominio Monodnaviria engloba a los virus ADN de una cadena.
El dominio Riboviria engloba a los virus que codifican polimerasas dependientes de ARN (virus ARN).
El dominio Varidnaviria engloba diversos virus ADN de doble cadena.
Las terminaciones son las siguientes:
- Dominio: -viria
- Reino: -virae
- Filo: -viricota
- Clase: -viricetes
- Orden: -virales
- Familia: -viridae
- Subfamilia: -virinae
- Género: -virus
Índice de contenidos
Taxonomía actual usando la clasificación ICTV
Esta es la taxonomía mediante la clasificación ICTV actual:
- Dominio Duplodnaviria
- Reino Heunggongvirae
- Filo Peploviricota
- Clase Herviviricetes
- Orden Herpesvirales
- Familia Alloherpesviridae
- Familia Herpesviridae
- Familia Malacoherpesviridae
- Orden Herpesvirales
- Clase Herviviricetes
- Filo Uroviricota
- Clase Caudoviricetes
- Orden Caudovirales
- Familia Ackermannviridae
- Familia Autographiviridae
- Familia Chaseviridae
- Familia Demerecviridae
- Familia Drexlerviridae
- Familia Herelleviridae
- Familia Myoviridae
- Familia Podoviridae
- Familia Siphoviridae
- Género Lilyvirus
- Orden Caudovirales
- Clase Caudoviricetes
- Filo Peploviricota
- Reino Heunggongvirae
- Dominio Monodnaviria
- Reino Loebvirae
- Filo Hofneviricota
- Clase Faserviricetes
- Orden Tubulavirales
- Familia Inoviridae
- Familia Plectroviridae
- Orden Tubulavirales
- Clase Faserviricetes
- Filo Hofneviricota
- Reino Sangervirae
- Reino Phixviricota
- Clase Malgrandaviricetes
- Orden Petitvirales
- Familia Microviridae
- Orden Petitvirales
- Clase Malgrandaviricetes
- Reino Phixviricota
- Reino Shotokuvirae
- Filo Cossaviricota
- Clase Mouviricetes
- Orden Polivirales
- Familia Bidnaviridae
- Orden Polivirales
- Clase Papovaviricetes
- Orden Sepolyvirales
- Familia Polyomaviridae
- Orden Zurhausenvirales
- Familia Papillomaviridae
- Orden Sepolyvirales
- Clase Quintoviricetes
- Orden Piccovirales
- Familia Parvoviridae
- Orden Piccovirales
- Clase Mouviricetes
- Filo Cressdnaviricota
- Clase Arfiviricetes
- Orden Baphvirales
- Familia Bacilladnaviridae
- Orden Cirlivirales
- Familia Circoviridae
- Orden Cremevirales
- Familia Smacoviridae
- Orden Mulpavirales
- Familia Nanoviridae
- Orden Recrevirales
- Familia Redondoviridae
- Orden Baphvirales
- Clase Repensiviricetes
- Orden Geplafuvirales
- Familia Geminiviridae
- Familia Genomoviridae
- Orden Geplafuvirales
- Clase Arfiviricetes
- Filo Cossaviricota
- Reino Trapavirae
- Filo Saleviricota
- Clase Huolimaviricetes
- Orden Haloruvirales
- Familia Pleolipoviridae
- Orden Haloruvirales
- Clase Huolimaviricetes
- Filo Saleviricota
- Reino Loebvirae
- Dominio Riboviria
- Reino Orthonavirae
- Filo Duplornaviricota
- Clase Chrymotiviricetes
- Orden Ghabrivirales
- Familia Chrysoviridae
- Familia Megabirnaviridae
- Familia Quadriviridae
- Familia Totiviridae
- Orden Ghabrivirales
- Clase Resentoviricetes
- Orden Reovirales
- Familia Reoviridae
- Orden Reovirales
- Clase Vidaverviricetes
- Orden Mindivirales
- Familia Cystoviridae
- Orden Mindivirales
- Clase Chrymotiviricetes
- Filo Kitrinoviricota
- Clase Alsuviricetes
- Orden Hepelivirales
- Familia Alphatetraviridae
- Familia Benyviridae
- Familia Hepeviridae
- Familia Matonaviridae
- Orden Martellivirales
- Familia Bromoviridae
- Familia Closteroviridae
- Familia Endornaviridae
- Familia Kitaviridae
- Familia Mayoviridae
- Familia Togaviridae
- Familia Virgaviridae
- Orden Tymovirales
- Familia Alphaflexiviridae
- Familia Betaflexiviridae
- Familia Deltaflexiviridae
- Familia Gammaflexiviridae
- Familia Tymoviridae
- Orden Hepelivirales
- Clase Flasuviricetes
- Orden Amarillovirales
- Familia Flaviviridae
- Orden Amarillovirales
- Clase Magsaviricetes
- Orden Nodamuvirales
- Familia Nodaviridae
- Familia Sinhaliviridae
- Orden Nodamuvirales
- Clase Tolucaviricetes
- Orden Tolivirales
- Familia Carmotetraviridae
- Familia Luteoviridae
- Familia Tombusviridae
- Orden Tolivirales
- Clase Alsuviricetes
- Filo Lenarviricota
- Clase Allassoviricetes
- Orden Levivirales
- Familia Leviviridae
- Orden Levivirales
- Clase Amabiliviricetes
- Orden Wolframvirales
- Familia Narnaviridae
- Orden Wolframvirales
- Clase Howeltoviricetes
- Orden Cryppavirales
- Familia Mitoviridae
- Orden Cryppavirales
- Clase Miaviricetes
- Orden Ourlivirales
- Familia Botourmiaviridae
- Orden Ourlivirales
- Clase Allassoviricetes
- Filo Negarnaviricota
- Subfilo Haploviricotina
- Clase Chunqiuviricetes
- Orden Muvirales
- Familia Qinviridae
- Orden Muvirales
- Clase Milneviricetes
- Orden Serpentovirales
- Familia Aspiviridae
- Orden Serpentovirales
- Clase Monjiviricetes
- Orden Jingchuvirales
- Familia Chuviridae
- Orden Mononegavirales
- Familia Artoviridae
- Familia Bornaviridae
- Familia Filoviridae
- Familia Lispiviridae
- Familia Mymonaviridae
- Familia Nyamiviridae
- Familia Paramyxoviridae
- Familia Pneumoviridae
- Familia Rhabdoviridae
- Familia Sunviridae
- Familia Xinmoviridae
- Orden Jingchuvirales
- Clase Yunchangviricetes
- Orden Goujianvirales
- Familia Yueviridae
- Orden Goujianvirales
- Clase Chunqiuviricetes
- Subfilo Polyploviricotina
- Clase Ellioviricetes
- Orden Bunyavirales
- Familia Arenaviridae
- Familia Cruliviridae
- Familia Fimoviridae
- Familia Hantaviridae
- Familia Leishbuviridae
- Familia Mypoviridae
- Familia Nairoviridae
- Familia Peribunyaviridae
- Familia Phasmaviridae
- Familia Phenuiviridae
- Familia Tospoviridae
- Familia Wupedeviridae
- Orden Bunyavirales
- Clase Insthoviricetes
- Orden Articulavirales
- Familia Amnoonviridae
- Familia Orthomyxoviridae
- Orden Articulavirales
- Clase Ellioviricetes
- Filo Pisuviricota
- Clase Duplopiviricetes
- Orden Durnavirales
- Familia Amalgaviridae
- Familia Hypoviridae
- Familia Partitiviridae
- Familia Picobirnaviridae
- Orden Durnavirales
- Clase Pisoniviricetes
- Orden Nidovirales
- Familia Abyssoviridae
- Familia Arteriviridae
- Familia Coronaviridae (Coronavirus)
- Familia Medioniviridae
- Familia Mesoniviridae
- Familia Mononiviridae
- Familia Euroniviridae
- Familia Roniviridae
- Familia Tobaniviridae
- Orden Nidovirales
- Clase Stelpaviricetes
- Orden Patatavirales
- Familia Potyviridae
- Orden Stellavirales
- Familia Astroviridae
- Orden Patatavirales
- Clase Duplopiviricetes
- Familia Birnaviridae
- Familia Permutotetraviridae
- Género Botybirnavirus
- Filo Duplornaviricota
- Reino Pararnavirae
- Filo Artverviricota
- Clase Revtraviricetes
- Orden Blubervirales
- Familia Hepadnaviridae
- Orden Ortervirales
- Familia Belpaoviridae
- Familia Caulimoviridae
- Familia Metaviridae
- Familia Pseudoviridae
- Familia Retroviridae
- Orden Blubervirales
- Clase Revtraviricetes
- Filo Artverviricota
- Familia Polymycoviridae
- Familia Sarthroviridae
- Género Albetovirus
- Género Aumaivirus
- Género Papanivirus
- Género Virtovirus
- Reino Orthonavirae
- Dominio Varidnaviria
- Reino Bamfordvirae
- Filo Nucleocytoviricota
- Clase Megaviricetes
- Orden Algavirales
- Familia Phycodnaviridae
- Orden Imitevirales
- Familia Mimiviridae
- Orden Pimascovirales
- Familia Ascoviridae
- Familia Iridoviridae
- Familia Marseilleviridae
- Orden Algavirales
- Clase Pokkesviricetes
- Orden Asfuvirales
- Familia Asfarviridae
- Orden Chitovirales
- Familia Poxviridae
- Orden Asfuvirales
- Clase Megaviricetes
- Filo Preplasmiviricota
- Clase Maveriviricetes
- Orden Priklausovirales
- Familia Lavidaviridae
- Orden Priklausovirales
- Clase Tectiliviricetes
- Orden Belfryvirales
- Familia Turriviridae
- Orden Kalamavirales
- Familia Tectiviridae
- Orden Rowavirales
- Familia Adenoviridae
- Orden Vinavirales
- Familia Corticoviridae
- Orden Belfryvirales
- Clase Maveriviricetes
- Filo Nucleocytoviricota
- Reino Helvetiavirae
- Filo Dividoviricota
- Clase Laserviricetes
- Orden Halopanivirales
- Familia Sphaerolipoviridae
- Orden Halopanivirales
- Clase Laserviricetes
- Filo Dividoviricota
- Reino Bamfordvirae
- Orden Ligamenvirales
- Familia Lipothrixviridae
- Familia Rudiviridae
- Familia Alphasatellitidae
- Familia Ampullaviridae
- Familia Anelloviridae
- Familia Avsunviroidae
- Familia Baculoviridae
- Familia Bicaudaviridae
- Familia Clavaviridae
- Familia Finnlakeviridae
- Familia Fuselloviridae
- Familia Globuloviridae
- Familia Guttaviridae
- Familia Halspiviridae
- Familia Hytrosaviridae
- Familia Nimaviridae
- Familia Nudiviridae
- Familia Ovaliviridae
- Familia Plasmaviridae
- Familia Polydnaviridae
- Familia Portogloboviridae
- Familia Pospiviroidae
- Familia Spiraviridae
- Familia Thaspiviridae
- Familia Tolecusatellitidae
- Familia Tristromaviridae
- Género Deltavirus
- Género Dinodnavirus
- Género Rhizidiovirus
La clasificación de las bacterias sigue siendo un campo en expansión que cambia de manera continua. Mediante la filogenia molecular y el análisis de la secuencia de genomas se han conseguido avances en la clasificación bacteriana, que antes del uso de estas tecnologías generaba bastante confusión.
Índice de contenidos
Clasificación de Bergey
La clasificación más aceptada es la del Manual de Bacteriología Sistemática de Bergey, que usaremos en esta web. Esta clasificación es denominada "The Taxonomic Outline of Bacteria and Archaea" (TOBA). La actualización más reciente de esta clasificación ordena a estos organismos en 11 partes, a saber:
Parte 1. Dominio Archaea
Engloba todo el dominio de las arqueas. Las diferencias que tienen con las bacterias es que su pared celular no tienen peptidoglicano, su membrana celular está formada por una monocapa lipídica, los lípidos están unidos al glicerol por enlaces éter y , a la hora de la traducción, el tRNA iniciador es el metionil-tRNA. En bacterias, su pared celular contiene peptidoglicano, su membrana celular está formada por una bicapa lipídica, los lípidos están unidos al glicerol por enlaces ester, y tRNA iniciador es el formilmetionil-tRNA.
El resto de partes son del dominio Bacteria.
Parte 2. Filos Aquificae, Thermotogae, Thermodesulfobacteria, Deinococcus-Thermus, Chrysiogenetes, Chloroflexi, Thermomicrobia, Nitrospira, Deferribacteres, Cyanobacteria, y Chlorobi
Engloban diversos grupos de bacterias hipertermófilas (Aquifex y el grupo Deinococcus-Thermus) y las bacterias fotosintéticas no proteobacterias.
Los 4 siguientes grupos están dedicados a las proteobacterias. Las proteobacterias son el mayor grupo de bacterias, y el más diverso. En él se agrupan la mayor parte de las bacterias de interés en medicina, industria o agricultura. La gran mayoría son GRAM negativas (-). Dentro de la página, estos grupos están organizados según su forma de vida.
- Proteobacterias quimiolitótrofas y metanótrofas
- Proteobacterias quimioorganótrofas aerobias
- Proteobacterias quimioorganótrofas anaerobias facultativas
- Rickettsias: otras proteobacterias (I)
- Otras protebacterias (II)
Así aparecen en el Manual de Bergey:
Parte 3. Filo Proteobacteria, clase Alphaproteobacteria
Parte 4. Filo Proteobacteria, clase Betaproteobacteria
Parte 5. Filo Proteobacteria, clase Gammaproteobacteria
Parte 6. Filo Proteobacteria, clases Deltaproteobacteria y Epsilonproteobacteria
Los 4 siguientes grupos están dedicados a los firmicutes. El filo Firmicutes destaca por ser GRAM+ en la mayoría de los casos y tener un bajo contenido de GC.
Parte 7. Filo Firmicutes, clase Clostridia
Bacterias GRAM+ con respiración anaerobia.
Parte 8. Filo Firmicutes, clase Mollicutes
Destacan por ser bacterias sin pared celular. Son pleomórficas, y las colonias tienen apariencia de huevo frito.
Parte 9. Filo Firmicutes, clase Bacilli
Bacterias GRAM+ con respiración aerobia.
Parte 10. Filo Actinobacteria, clase Actinobacteria
Son bacterias GRAM+. Destacan por tener especies con capacidad de generar antibióticos naturales.
Parte 11. Filos Planctomycetes, Chlamydiae, Spirochaetes, Fibrobacteres, Acidobacteria, Bacteroidetes, Fusobacteria, Verrucomicrobia, Dictyoglomi, Gemmatomonadetes, y Lentisphaerae.
Bacteras GRAM- sin relación entre si.
También hay otras clasificaciones que, si bien no son oficiales, ayudan a entender mejor el mundo de las bacterias.
Clasificación en función de su dependencia de oxígeno (respiración)
Aerobios estrictos. Estos microorganismos requieren y dependen del oxígeno siempre, que actúa como aceptor final de electrones. Son SOD+ y catalasa+.
Microaerófilos. Necesitan oxígeno por debajo de la concentración atmosférica. Respiran y fermentan. Son SOD+ y catalasa+/- (niveles bajos).
Anaerobios facultativos. Usan el oxígeno cuando está disponible, pero también pueden vivir en ausencia de él. Su metabolismo depende de la presencia de oxígeno. Si hay oxígeno respiran, y crecen más; mientras que si no hay oxígeno fermentan, y crecen menos. Son SOD+ y catalasa+.
Anaerobios aerotolerantes. Estos microorganismos siempre tienen un metabolismo fermentativo. No usan el oxígeno, pero no les es tóxico. Son SOD+ y catalasa-.
Anaerobios obligados. Estos microorganismos siempre fermentan. No toleran el oxígeno, es tóxico para ellos. Son SOD- y catalasa-.
Los microorganismos que viven en presencia de oxígeno necesitan protegerse de él. Por ello, los aerobios estrictos y anaerobios facultativos suelen contener las enzimas superóxido dismutasa (SOD), que cataliza la destrucción de los radicales de oxígeno (O2), y catalasa, que cataliza la destrucción de los radicales de peróxido de oxígeno (H2O2). Ambos procesos liberan oxígeno. Los anaerobios aerotolerantes pueden carecer de catalasa, pero cuentan con peroxidasas que reducen el peróxido de oxígeno también, aunque sin liberar oxígeno.
Clasificación en función de su fuente de energía
Fotótrofos. Usan la luz solar y la convierten en energía química.
Quimiótrofos. Dependen de sustancias químicas para obtener energía química.
Clasificación en función de su fuente de carbono
Autótrofos. Usan el dióxido de carbono (CO2), ya que pueden fijarlo.
Heterótrofos. Usan compuestos orgánicos, ya que no pueden fijar CO2.
Clasificación en función de su fuente de energía y de carbono
Fotoautótrofos. Su fuente de energía es la luz solar y la fuente de carbono es el CO2. El poder reductor para reducir el dióxido de carbono lo suministra el agua, por lo que este mecanismo fotosintético desprende oxígeno. Es propio de plantas, algas y cianobacterias.
Fotoheterótrofos. Su fuente de energía es la luz solar y la fuente de carbono es algún compuesto orgánico. El poder reductor para reducir el carbono orgánico lo suministran moléculas reducidas como el hidrógeno (H2) o el ácido sulfhídrico (H2S), por lo que este mecanismo fotosintético no desprende oxígeno. Es propio de bacterias rojas y algunas bacterias verdes.
Quimioautótrofos. Su fuente de energía son las sales orgánicas y la fuente de carbono es el CO2. El sustrato del que obtienen energía también les sirve como fuente de carbono. Se les conoce coloquialmente como "comedores de piedras". Es propio de diversas bacterias como las del azufre, las bacterias del nitrógeno, las bacterias del hidrógeno, y las bacterias del hierro.
Quimioheterótrofos. Su fuente de energía y de carbono es algún compuesto orgánico. La mayor parte de los seres vivos, incluidas la mayoría de bacterias, se incluyen en este grupo.
Mixótrofos. Hay algunas especies que tienen un metabolismo mixto. Por ejemplo, alguna especie de Beggiatoa usa compuestos orgánicos como fuente de carbono y alguna sal como fuente de energía.
Clasificación según la tinción de GRAM
La tinción de GRAM es una tinción diferencial, que distingue a las bacterias por morfología y composición. Según esta tinción, las bacterias se dividen en:
Bacterias GRAM positivas. Su capa de peptidoglicano es muy gruesa, pudiendo llegar a ocupar hasta el 90% de la pared celular. En estas bacterias aparece un polímeros exclusivos, los ácidos teicoicos. Al microscopio con la tinción de GRAM, estas bacterias se ven de color violeta.
Bacterias GRAM negativas. No tienen ácidos teicoicos. Su capa de peptidoglicano es más pequeña, y ocupa menos de un 10% de la pared celular. Cuentan con una membrana externa que rodea al peptidoglicano. Vemos componentes exclusivos de las bacterias GRAM negativas, como la lipoproteína de Brown, las uniones de Bayer y los lipopolisacáridos. Al microscopio con la tinción de GRAM, estas bacterias se ven de color naranja o rojo.
En general las bacterias GRAM negativas son más resistentes que las GRAM positivas a la acción de los antibióticos, ya que su membrana externa es más hidrofóbica, más impermeable al paso de sustancias.
La clasificación del Comité Internacional de Taxonomía de Virus (siglas ICTV en inglés) utiliza una forma de clasificar muy parecida a la que se hace con los seres vivos. Así, los virus se clasifican por orden, familia, subfamilia, género y especie.
Solo existe el reino Riboviria, grupo taxonómico que agrupa a los virus ARN y los viroides. De la clasificación de Baltimore están representados los grupos III, IV y V. La primera parte de su nombre ribo proviene de ácido ribonucleico (ARN). Es el primer reino de virus propuesto. En el futuro puede añadirse los virus de ADN pero se sigue investigando.
Actualización: Los virus se clasifican en 4 dominios, 9 reinos y 16 filos. Para ver la nueva clasificación, haz clic aquí.
Las terminaciones son las siguientes:
- Dominio: -viria
- Reino: -virae
- Filo: -viricota
- Clase: -viricetes
- Orden: -virales
- Familia: -viridae
- Subfamilia: -virinae
- Género: -virus
Esta es la taxonomía mediante la clasificación ICTV actual:
- Reino Riboviria
- Filo Negarnaviricota
- Subfilo Haploviricotina
- Clase Chunqiuviricetes
- Orden Muvirales
- Familia Qinviridae
- Orden Muvirales
- Clase Milneviricetes
- Orden Serpentovirales
- Familia Chuviridae
- Orden Serpentovirales
- Clase Monjiviricetes
- Orden Jingchuvirales
- Familia Chuviridae
- Orden Mononegavirales
- Familia Artoviridae
- Familia Bornaviridae
- Familia Filoviridae
- Familia Lispiviridae
- Familia Mymonaviridae
- Familia Nyamiviridae
- Familia Paramyxoviridae
- Familia Pneumoviridae
- Familia Rhabdoviridae
- Familia Sunviridae
- Familia Xinmoviridae
- Orden Jingchuvirales
- Clase Yunchangviricetes
- Orden Goujianvirales
- Familia Yueviridae
- Orden Goujianvirales
- Clase Chunqiuviricetes
- Subfilo Polyploviricotina
- Clase Ellioviricetes
- Orden Bunyavirales
- Familia Arenaviridae
- Familia Cruliviridae
- Familia Fimoviridae
- Familia Hantaviridae
- Familia Leishbuviridae
- Familia Mypoviridae
- Familia Nairoviridae
- Familia Peribunyaviridae
- Familia Phasmaviridae
- Familia Phenuiviridae
- Familia Tospoviridae
- Familia Wupedeviridae
- Orden Bunyavirales
- Clase Insthoviricetes
- Orden Articulavirales
- Familia Amnoonviridae
- Familia Orthomyxoviridae
- Orden Articulavirales
- Clase Ellioviricetes
- Subfilo Haploviricotina
- Filo Negarnaviricota
- Orden Nidovirales
- Familia Abyssoviridae
- Familia Arteriviridae
- Familia Coronaviridae (Coronavirus)
- Familia Medioniviridae
- Familia Mesoniviridae
- Familia Mononiviridae
- Familia Euroniviridae
- Familia Roniviridae
- Familia Tobaniviridae
- Orden Picornavirales
- Familia Dicistroviridae
- Familia Iflaviridae
- Familia Marnaviridae
- Familia Picornaviridae
- Familia Polycipiviridae
- Familia Secoviridae
- Orden Tymovirales
- Familia Alphaflexiviridae
- Familia Betaflexiviridae
- Familia Deltaflexiviridae
- Familia Gammaflexiviridae
- Familia Tymoviridae
- Familias no asignadas
- Familia Amalgaviridae
- Familia Alphatetraviridae
- Familia Alvernaviridae
- Familia Astroviridae
- Familia Avsunviroidae
- Familia Barnaviridae
- Familia Benyviridae
- Familia Birnaviridae
- Familia Botourmiaviridae
- Familia Bromoviridae
- Familia Caliciviridae
- Familia Carmotetraviridae
- Familia Chrysoviridae
- Familia Closteroviridae
- Familia Cystoviridae
- Familia Endornaviridae
- Familia Flaviviridae
- Familia Hepeviridae
- Familia Hypoviridae
- Familia Kitaviridae
- Familia Leviviridae
- Familia Luteoviridae
- Familia Matonaviridae
- Familia Megabirnaviridae
- Familia Narnaviridae
- Familia Nodaviridae
- Familia Partitiviridae
- Familia Permutotetraviridae
- Familia Picobirnaviridae
- Familia Pospiviroidae
- Familia Potyviridae
- Familia Quadriviridae
- Familia Reoviridae
- Familia Sarthroviridae
- Familia Solemoviridae
- Familia Solinviviridae
- Familia Togaviridae
- Familia Tombusviridae
- Familia Totiviridae
- Género Botybirnavirus
- Familia Virgaviridae
- Géneros no asignados
- Albetovirus
- Aumaivirus
- Idaeovirus
- Papanivirus
- Sinaivirus
- Virtovirus
Para ver la nueva clasificación, puedes hacerlo en nuestra nueva página de la clasificación ICTV actualizada.
El Sistema de Clasificación de Baltimore fue propuesto por David Baltimore. Está basada en el tipo de ácido nucleico de los virus (ADN o ARN) y su modo de expresión génica; en otras palabras, se clasifica según su material genético.
Si has visto el ciclo de los virus, habrás observado que el proceso de replicación de los virus difería en función de su grupo. En nuestra página de replicación de los virus puedes ver las diferencias de cada grupo.
En este artículo verás expresiones a las abreviaturas en inglés de ADN y ARN: DNA y RNA. Si eres estudiante de biología, microbiología, o algo similar esto no te pillará de sorpresa. No obstante, puede que haya gente que le siga sonando más natural la abreviatura española...conforme se avanza en los estudios, estas cosas cambian 😅
Según la Clasificación Baltimore, los virus se distribuyen en siete grupos:
Índice de contenidos
Grupo I: Virus DNA bicatenario (virus dsDNA)
Son virus DNA de doble cadena. La replicación del DNA del virus se realiza por medio de las DNA-polimerasas dependiente de DNA del huésped o codificadas por el virus. Son los virus más comunes, y los más diversos. Esta es su taxonomía:
- Orden Caudovirales
- Familia Ackermannviridae
- Familia Herelleviridae
- Familia Myoviridae
- Familia Podoviridae
- Familia Siphoviridae
- Orden Herpesvirales
- Familia Alloherpesviridae
- Familia Herpesviridae
- Familia Malacoherpesviridae
- Orden Ligamenvirales
- Familia Lipothrixviridae
- Familia Rudiviridae
- Familias no asignadas
- Familia Adenoviridae
- Familia Ampullaviridae
- Familia Ascoviridae
- Familia Asfarviridae
- Familia Baculoviridae
- Familia Bicaudaviridae
- Familia Clavaviridae
- Familia Corticoviridae
- Familia Fuselloviridae
- Familia Globuloviridae
- Familia Guttaviridae
- Familia Hytrosaviridae
- Familia Iridoviridae
- Familia Lavidaviridae
- Familia Marseilleviridae
- Familia Medusaviridae1
- Familia Mimiviridae
- Familia Nimaviridae
- Familia Nudiviridae
- Familia Ovaliviridae
- Familia Papillomaviridae
- Familia Phycodnaviridae
- Familia Plasmaviridae
- Familia Pleolipoviridae [dsDNA; ssDNA]
- Familia Polydnaviridae
- Familia Polyomaviridae
- Familia Portogloboviridae
- Familia Poxviridae
- Familia Sphaerolipoviridae
- Familia Tectiviridae
- Familia Tristromaviridae
- Familia Turriviridae
- Géneros no asignados
- Dinodnavirus
- Rhizidiovirus
- Salterprovirus
Grupo II: Virus DNA monocatenario (virus ssDNA)
Son virus DNA de una cadena. Al igual que el grupo I, la replicación del DNA del virus se realiza por medio de las DNA-polimerasas dependiente de DNA. La cadena de DNA puede ser diferente en los virus, así que dentro de este grupo los virus se pueden clasificar en:
- Virus ssDNA. La cadena de DNA monocatenario no tiene polaridad o tiene polaridad mixta.
- Virus ssDNA(+). Cadena de DNA de polaridad positiva. Esto ocurre cuando una versión de ARN de la misma secuencia es traducible en proteínas
- Virus ssDNA(-). Cadena de DNA de polaridad negativa. El caso contrario al anterior.
- Virus ssDNA(+/-). Cadena de DNA de polaridad ambisentido. El genoma contiene ambos sentidos, positivo y negativo.
Esta es su taxonomía, formada por familias aún no asignadas:
- Familia Alphasatellitidae [ssDNA]
- Familia Anelloviridae [ssDNA(-)]
- Familia Bacilladnaviridae [ssDNA]
- Familia Bidnaviridae [ssDNA]
- Familia Circoviridae [ssDNA(+/-)]
- Familia Geminiviridae [ssDNA(+/-)]
- Familia Genomoviridae [ssDNA]
- Familia Inoviridae [ssDNA(+)]
- Familia Microviridae [ssDNA(+)]
- Familia Nanoviridae [ssDNA(+)]
- Familia Parvoviridae [ssDNA(+)]
- Familia Pleolipoviridae [dsDNA; ssDNA]
- Familia Smacoviridae [ssDNA]
- Familia Spiraviridae [ssDNA(+)]
- Familia Tolecusatellitidae [ssDNA]
Grupo III: Virus RNA bicatenario (virus dsRNA)
Son virus RNA de doble cadena. Los virus de este grupo se replican en el citoplasma y no dependen de las polimerasas de las células huésped, a diferencia de los virus DNA, ya que incluyen las enzimas necesarias en el virión. Esta es su taxonomía:
- Familias no asignadas
- Familia Amalgaviridae
- Familia Birnaviridae
- Familia Chrysoviridae
- Familia Cystoviridae
- Familia Endornaviridae
- Familia Megabirnaviridae
- Familia Partitiviridae
- Familia Picobirnaviridae
- Familia Quadriviridae
- Familia Reoviridae
- Familia Totiviridae
- Géneros no asignados
- Botybirnavirus
Grupo IV: Virus RNA monocatenario positivo (virus ssRNA(+))
Son virus RNA de una cadena. Los virus de este grupo se replican en el citoplasma; a diferencia de los virus DNA, no son tan dependientes del huésped, ni usan DNA intermedio para replicarse. Su cadena de RNA tiene polaridad positiva lo que significa que son idénticos al mRNA viral, así que pueden ser traducidos inmediatamente por el hospedador. Esta es su taxonomía:
- Orden Nidovirales
- Familia Abyssoviridae
- Familia Arteriviridae
- Familia Coronaviridae
- Familia Medioniviridae
- Familia Mesoniviridae
- Familia Mononiviridae
- Familia Euroniviridae
- Familia Roniviridae
- Familia Tobaniviridae
- Orden Picornavirales
- Familia Dicistroviridae
- Familia Iflaviridae
- Familia Marnaviridae
- Familia Picornaviridae
- Familia Polycipiviridae
- Familia Secoviridae
- Orden Tymovirales
- Familia Alphaflexiviridae
- Familia Betaflexiviridae
- Familia Deltaflexiviridae
- Familia Gammaflexiviridae
- Familia Tymoviridae
- Familias no asignadas
- Familia Alphatetraviridae
- Familia Alvernaviridae
- Familia Astroviridae
- Familia Barnaviridae
- Familia Benyviridae
- Familia Botourmiaviridae
- Familia Bromoviridae
- Familia Caliciviridae
- Familia Carmotetraviridae
- Familia Closteroviridae
- Familia Flaviviridae
- Familia Hepeviridae
- Familia Hypoviridae
- Familia Kitaviridae
- Familia Leviviridae
- Familia Luteoviridae
- Familia Matonaviridae
- Familia Narnaviridae
- Familia Nodaviridae
- Familia Permutotetraviridae
- Familia Potyviridae
- Familia Sarthroviridae
- Familia Solemoviridae
- Familia Solinviviridae
- Familia Togaviridae
- Familia Tombusviridae
- Familia Virgaviridae
- Géneros no asignados
- Albetovirus
- Aumaivirus
- Idaeovirus
- Papanivirus
- Sinaivirus
- Virtovirus
Grupo V: Virus RNA monocatenario negativo (virus (-)ssRNA)
Son virus RNA de una cadena. Los virus de este grupo no usan DNA intermedio para replicarse. El RNA viral es negativo, lo que significa que es complementario del mRNA, así que debe convertirse en RNA positivo por una RNA polimerasa antes de la traducción. Puesto que es necesario el proceso de transformación del RNA a positivo, el RNA 'original' del virus no es en si mismo infeccioso. Aquí se incluyen también a los virus RNA monocatenarios ambisentido (sentido postivo y negativo: virus ssRNA(+/-)). Esta es su taxonomía:
- Subfilo Haploviricotina
- Clase Chunqiuviricetes
- Orden Muvirales
- Familia Qinviridae
- Orden Muvirales
- Clase Milneviricetes
- Orden Serpentovirales
- Familia Chuviridae
- Orden Serpentovirales
- Clase Monjiviricetes
- Orden Jingchuvirales
- Familia Chuviridae
- Orden Mononegavirales
- Familia Artoviridae
- Familia Bornaviridae
- Familia Filoviridae
- Familia Lispiviridae
- Familia Mymonaviridae
- Familia Nyamiviridae
- Familia Paramyxoviridae
- Familia Pneumoviridae
- Familia Rhabdoviridae
- Familia Sunviridae
- Familia Xinmoviridae
- Orden Jingchuvirales
- Clase Yunchangviricetes
- Orden Goujianvirales
- Familia Yueviridae
- Orden Goujianvirales
- Clase Chunqiuviricetes
- Subfilo Polyploviricotina
- Clase Ellioviricetes
- Orden Bunyavirales
- Familia Arenaviridae
- Familia Cruliviridae
- Familia Fimoviridae
- Familia Hantaviridae
- Familia Leishbuviridae
- Familia Mypoviridae
- Familia Nairoviridae
- Familia Peribunyaviridae
- Familia Phasmaviridae
- Familia Phenuiviridae
- Familia Tospoviridae
- Familia Wupedeviridae
- Orden Bunyavirales
- Clase Insthoviricetes
- Orden Articulavirales
- Familia Amnoonviridae
- Familia Orthomyxoviridae
- Orden Articulavirales
- Clase Ellioviricetes
Grupo VI: Virus RNA monocatenario retrotranscrito (virus ssRNA-RT)
Son virus RNA de una cadena. Lo que tiene de especial este grupo de virus es que se replica mediante un proceso llamado 'transcripción inversa': se forma DNA a partir del RNA original por medio de una enzima llamada transcriptasa inversa. En este grupo hay se usa un intermediario de DNA aunque sea un virus RNA, a diferencia de los virus RNA vistos anteriormente. Esta es su taxonomía:
- Orden Ortervirales (ssRNA-RT; dsDNA-RT)
- Familia Belpaoviridae
- Familia Metaviridae
- Familia Pseudoviridae
- Familia Retroviridae
Grupo VII: Virus DNA bicatenario retrotranscrito (virus dsDNA-RT)
Son virus DNA de doble cadena. Este grupo de virus replica el material genético mediante la 'transcripción inversa': se forma RNA a partir del DNA original; este RNA vuelve a convertirse en DNA por medio de la transcriptasa inversa. En este grupo hay se usa un intermediario de RNA aunque sea un virus DNA, a diferencia de los virus DNA vistos anteriormente. Esta es su taxonomía:
- Orden Ortervirales (ssRNA-RT; dsDNA-RT)
- Familia Caulimoviridae
- Familias no asignadas
- Familia Hepadnaviridae
La nomenclatura viral ha sido muy confusa a lo largo de la historia debido a la naturaleza extraña de los virus. Muchos virus han sido nombrados en función de la enfermedad que producen (herpes); otros han recibido el nombre de su descubridor (virus de Epstein-Barr), y otros hacen referencia al lugar en el que han sido descubiertos (fiebre del Nilo).
Actualmente hay dos clasificaciones aprobadas por el Comité Internacional de Taxonomía de Virus:
Índice de contenidos
Clasificación Baltimore
El Sistema de Clasificación Baltimore fue propuesto por David Baltimore. Está basada en el tipo de ácido nucleico de los virus (ADN o ARN) y su modo de... Leer más.
Clasificación ICTV
La clasificación del Comité Internacional de Taxonomía de Virus (siglas ICTV en inglés) utiliza una forma de clasificar muy parecida a la que se hace con... Leer más.
Clasificación ICTV (nueva)
La clasificación del Comité Internacional de Taxonomía de Virus (siglas ICTV en inglés) utiliza una forma de clasificar muy parecida a la que se hace con... Leer más.
Otras clasificaciones (no oficiales)
Otra forma común de clasificación es en función del hospedador al que infectan. Si tienes microbiología como asignatura, seguramente esta forma de clasificación sea la que se usa. Este será el modo de organización en los menús de esta página. En este caso, los virus se clasifican en:
También se puede clasificar en función de algunas de sus estructuras.
Otra forma de clasificación es en función de su cápside (para más información sobre la cápside viral mira el apartado de tamaño y composición). En este caso los virus se clasifican en:
- Virus helicoidales.
- Virus icosaédricos.
- Virus complejos.
También podemos clasificar a los virus en función de su envoltura (para más información sobre la envoltura mira el apartado de tamaño y composición). En este caso los virus se clasifican en:
- Virus envueltos. Virus con envuelta.
- Virus desnudos. Virus sin envuelta.
Dentro de la sección de bacterias daremos información sobre el dominio Bacteria y el dominio Archaea. Aunque la bacteriología estudia las bacterias (y le da nombre a esta ciencia) también estudia a la arqueas. Así que podemos decir que la bacteriología estudia a los organismos procariotas.
Dentro de los procariotas, lo que podríamos decir que es microbiología general, hemos visto:
¿Qué es una bacteria?
Las bacterias son organismos unicelulares sin núcleo. El dominio Bacteria se engloba dentro del superreino Prokaryota, junto al dominio Archaea. Esto significa que son organismos procariotas, no tienen un núcleo definido ni (en general) tienen orgánulos membranosos internos. Su tamaño oscila entre los 0,5 y 5 μm de longitud, por lo que es necesario un microscopio para su observación. Tienen diversas morfologías, pudiendo ser esféricas, barras, filamentosas, curvadas o helicoidales. La célula procariota es diferente a la de eucariotas y su nutrición puede ser variada.
Las bacterias son los seres vivos más abundantes del planeta. Se encuentran y se desarrollan en todos los ambientes terrestres y acuáticos, incluyendo los más extremos (calor o frío extremo, zonas radiactivas, lugares de gran presión...). También están en el cuerpo humano, si bien la mayoría son inofensivas, y algunas también nos son beneficiosas.
Clasificación de las bacterias
Conociendo todo esto, será más fácil entender esta sección. La clasificación oficial usada por la bacteriología es la clasificación de Bergey, abreviada como TOBA. En este sistema, que consta de varias partes, una de ellas está dedicada a las arqueas. Si quieres ver la clasificación TOBA entera puedes consultarla en Wiley Online Library. Eso sí, necesitarás contar con una cuenta de universidad😅
En la clasificación de Bergey se engloban a las arqueas también. De ahí que la bacteriología abarque el estudio de bacterias y arqueas. Ahora bien, éstas son diferentes. Las diferencias que tienen con las bacterias es que su pared celular no tienen peptidoglicano, su membrana celular está formada por una monocapa lipídica, los lípidos están unidos al glicerol por enlaces éter y , a la hora de la traducción, el tRNA iniciador es el metionil-tRNA. En bacterias, su pared celular contiene peptidoglicano, su membrana celular está formada por una bicapa lipídica, los lípidos están unidos al glicerol por enlaces ester, y tRNA iniciador es el formilmetionil-tRNA. En la página dedicada a arqueas tienes una sección donde se detallan más todas las diferencias que tienen.
En esta página, hemos agrupado a los procariotas en estos grupos:
- Clasificación de las bacterias (Clasificación de Bergey y otras no oficiales)
- Dominio Archaea
- Dominio Bacteria
- Aquifex y el grupo Deinococcus-Thermus
- Bacterias fotosintéticas
- Proteobacterias quimiolitótrofas y metanótrofas
- Proteobacterias quimiorganótrofas aerobias
- Proteobacterias quimiorganótrofas anaerobias
- Las Rickettsias; otras proteobacterias (1)
- Otras proteobacterias (2)
- Firmicutes (GRAM+ con bajo contenido en G+C)
- Actinobacterias (GRAM+ con alto contenido en G+C)
- Otras bacterias (volumen V)
Este orden es bastante usado para su estudio en la universidad, por lo que a algunos os puede resultar familiar.
Una vez hayas visto todo lo relacionado con bacterias, quizá quieras ver otros microorganismos, como los eucariotas. También puedes ver todo lo relacionado con virus. Presentan una relación íntima con las bacterias, ya que algunos de ellos, conocidos como bacteriófagos, les infectan. Es un proceso de coevolución en que ambos elementos se adaptan a su contrincante.
